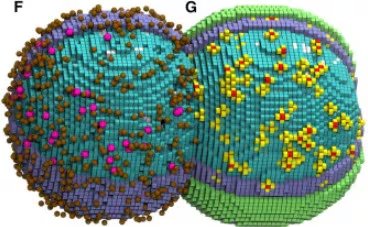
En un entorno tecnológico de vanguardia, una bacteria de dimensiones microscópicas se replica con la exactitud de un cronómetro. No se trata de una producción cinematográfica, sino del éxito de una investigación que ha logrado la simulación digital íntegra de una célula, recreada molécula a molécula durante la totalidad de su ciclo de existencia. Este avance, liderado por los investigadores Zane R. Thornburg y Andrew Maytin del J. Craig Venter Institute (JCVI) y la Universidad de Illinois, redefine los límites de la biología computacional y establece el inicio de una etapa transformadora en el estudio de los seres vivos.
El foco de este logro es la JCVI-Syn3A, una bacteria que posee el genoma más elemental identificado hasta la fecha, constituido por apenas 493 genes. Esta célula sintética, estructurada para contener únicamente los componentes indispensables para la vida, funcionó como el modelo perfecto para un desafío mayúsculo: mapear cada interacción química y el desplazamiento físico de todos sus elementos a lo largo de 105 minutos de existencia.
Los detalles de la simulación, expuestos en la publicación científica Cell, revelaron que se requirieron seis días de procesamiento en sistemas de supercomputación para reconstruir un ciclo de vida que, en condiciones naturales, ocurre en menos de dos horas.
“La complejidad de la biología supera con creces nuestra capacidad de procesamiento actual”
, admitió Thornburg ante el reto técnico enfrentado.
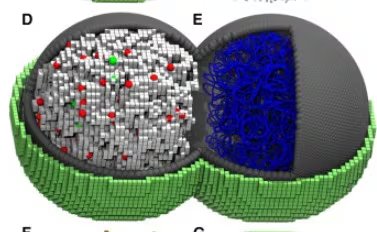
Un ciclo de vida reconstruido con precisión molecular
Para alcanzar este grado de fidelidad, el equipo de expertos combinó complejos modelos matemáticos con simulaciones espaciales cinéticas, empleando unidades de procesamiento gráfico (GPU) de última generación. A través de estas herramientas, pudieron monitorear la ubicación y el rol de cada ribosoma y de las cadenas de ADN en el interior celular, además de recrear procesos fundamentales como la síntesis de proteínas y la replicación genómica.
La implementación de una simulación en 4D —que integra la variable temporal a las tres dimensiones físicas— permitió detectar que, incluso en los organismos más simples, las reacciones químicas operan bajo patrones determinados y no de forma azarosa.
“La organización espacial es el mecanismo crítico que evita el colapso metabólico de la célula, permitiendo que los recursos lleguen a donde se necesitan en el momento preciso de la división”
, detalló Thornburg sobre los hallazgos.
Más allá de ser una simple lista de material genético, esta célula virtual demostró que la existencia depende de una coreografía molecular donde la posición exacta de cada partícula define si la división celular será exitosa. Los resultados arrojaron luz sobre fenómenos que la experimentación tradicional no puede visualizar, como la distribución heterogénea de metabolitos en el citoplasma.
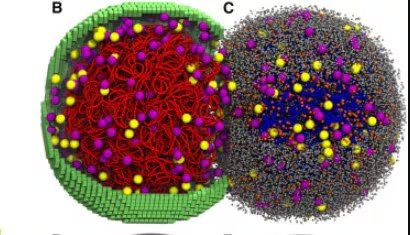
La profesora Zaida Luthey-Schulten, coautora de la investigación, señaló:
“La capacidad de capturar con precisión las condiciones en constante cambio dentro de una célula viva abre una nueva ventana a los fundamentos de los sistemas vivos”
. Gracias a este modelo, ahora es posible predecir cómo reacciona la célula ante múltiples experimentos de forma simultánea, abarcando desde la biogénesis de ribosomas hasta el metabolismo de los nucleótidos.
El desafío tecnológico de la biología virtual
Este trabajo evidencia la escala exponencial de la complejidad biológica. El hecho de que una célula con menos de 500 genes demande días de supercomputación sugiere que simular una célula humana —que cuenta con aproximadamente 20.000 genes— representa un desafío científico de una dimensión totalmente distinta.
Asimismo, el modelo digital confirmó que cada célula simulada es única, producto de la variabilidad natural de los procesos biológicos, un factor clave para entender mejor la diversidad en el comportamiento celular.
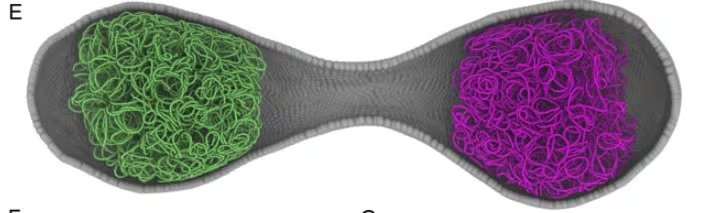
La recreación de la JCVI-Syn3A trasciende el hito técnico, pues ofrece un entorno seguro para testear nuevas terapias farmacológicas y genéticas, facilitando el camino hacia una medicina personalizada.
“Por primera vez, tenemos un avatar digital que se divide igual que su contraparte biológica”
, puntualizó Thornburg.
El estudio plantea que el porvenir de la simulación celular estará impulsado por la inteligencia artificial, capaz de procesar la base de datos obtenida para anticipar respuestas celulares ante mutaciones o fármacos. De esta manera, la brecha entre informática y biología se reduce, permitiendo ensayos en laboratorios virtuales antes de actuar sobre organismos reales.
Para los autores, este proyecto marca un punto de inflexión. La capacidad de simular la vida completa de una célula mínima constituye la prueba definitiva para el conocimiento científico actual y una vía para descifrar el código molecular que convierte la materia en vida.
Fuente: Fuente